機能詳細3 受容体構造に基づく分子設計1 —探索と設計—
新規リガンドの探索
ドッキングシミュレーション
標的タンパク質の活性部位において、化合物の配座を探索し、化合物の安定な結合配座を予測します。評価関数には、静電、ファンデルワールス、溶媒和の各相互作用エネルギーと、接触表面積に基づいた関数、電子密度マップとの重なりに基づいた関数などから選択できます。タンパク質構造を可動にしたInduced-Fitドッキングにも対応しています。タンパク質の活性部位における化合物の配座の探索のために、以下の手法が搭載されています。
- 標準のドッキング
複合体構造のリガンド周辺やポケット探索で得られたアルファ球を基準に化合物を配置します。 - テンプレートドッキング
標的タンパク質とリガンドの共結晶構造におけるリガンドの部分構造や類似原子を基準として化合物を配置します。 - 電子密度フィッティング
電子密度と重なるように化合物の配置と構造最適化計算を行います。 - Covalent Docking
活性部位に化合物を配置し、化学反応式に従って標的タンパク質と共有結合させます。化学反応式の編集や追加、標的タンパク質の反応部位の指定ができます。 - タンパク質(核酸)ータンパク質ドッキング
タンパク質あるいは核酸をリガンドとして、受容体との結合様式を予測します。 - 外部プログラムの利用
活性部位への化合物の配置に、外部のドッキングプログラム (FlexX 、GOLD、Surflex-Dock) を利用できます。
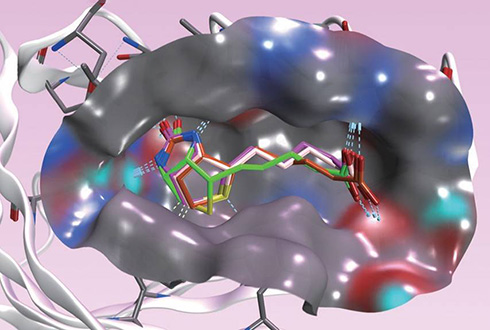
フラグメント結合位置検索
受容体のポケット内でフラグメントが安定に存在できる位置を求めます。
複数のフラグメントを同時に探索し、結果をde novoデザインに利用することができます。
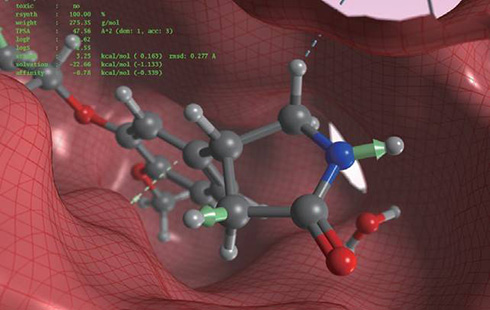
新規リガンドの設計
結合部位での分子設計
リガンドに官能基や置換基を付加することができる位置をモニタリングしながらリガンドを改変し、リガンドのひずみエネルギー、分子量、TPSA、logS 、logP、logD(pH7の条件でのlogP) 、変異原性、受容体との親和性を表示します。ライブラリーからの置換基の自動探索や、サードパーティの2Dスケッチャーを用いた分子構造の改変を行うことも可能です。
ペプチドリガンドの探索
ペプチド受容体の複合体構造より、ペプチドの変異体を自動的に構築し、さらにペプチドの安定性や受容体との親和性を計算します。目的に応じたペプチドリガンドを設計する際に利用できます。
分子フラグメントデータベース
付属の76万件のフラグメント構造データベースや81万件のChEMBL※1フラグメントデータベースが提供されています。これらをフラグメントデータベースの分子設計に利用することが出来ます。
フラグメントベースの分子設計
リガンドを構成するフラグメント構造を組み合わせることで、新規リガンド候補構造を生成します。CAVEAT法※2に基づいて、結合する分子の位置を予測し、タンパク質の構造に適合するようにリガンド構造の改変を行います。環化や環縮合の指定も可能です。生成させたリガンド候補化合物に対して、分子記述子、QSARモデル式、ファーマコフォアモデルによるフィルタリングや、タンパク質ポケット内での構造最適化を行い、受容体との親和性や合成可能性スコアの良好な候補化合物を選出できます。
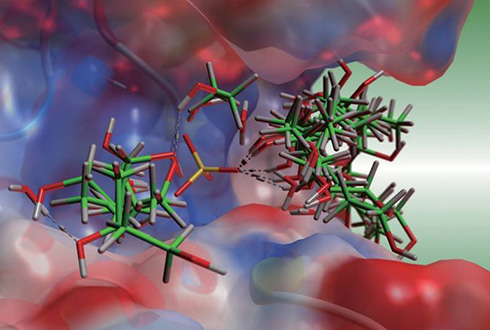
- 凝固因子Xaについて行った母核構造置換。淡青網球は保存したい水素結合受容体の位置。受容体の立体障害を考慮し、リガンドの両端部をつなぐ母核構造を探索。
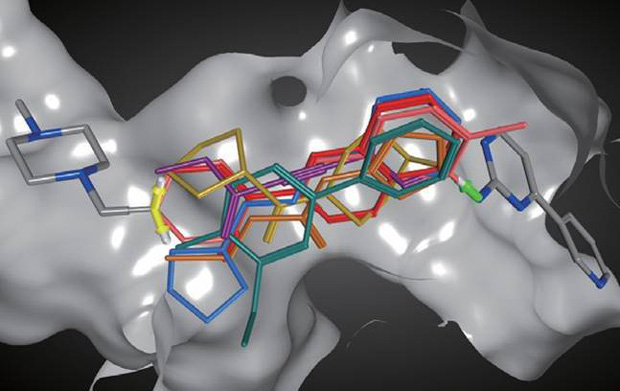
- 2つのフラグメントをつなぐリンカーを探索。2種類のベクトル(緑、黄)により結合の方向と組み合わせを指定。
- 母核構造変換
リガンドの母核構造を他の構造に置き換えます。タンパク質との相互作用が良好な置換基はそのままにして、新しい骨格を持つリガンド候補化合物を生成します。 - フラグメント付加
リガンドの任意の位置にフラグメント構を造付加します。適切な相互作用を形成するフラグメント構造で活性部位の空間を充填したリガンド候補化合物が得られます。 - フラグメント連結
配置された複数のフラグメント構造を連結するリンカー構造を探索します。活性部位内のそれぞれの相互作用部位に配置されたフラグメント構造とリンカー構造から、適切なリガンド候補化合物を生成できます。 - 構造変換ルールによる新規分子への展開
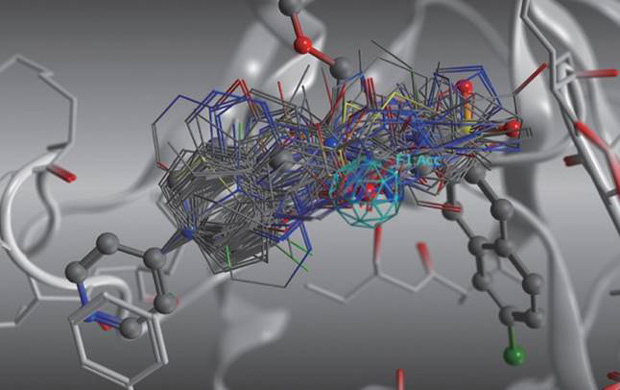
生物学的等価体やその他の構造変換ルールに基づいて、部分構造を他の構造に置換します。メディシナルケミストの知見を反映した構造展開が可能です。変換ルールはRXNファイルを用いて追加、編集が可能です。 - フラグメント交換 (BREED※3)
既知のリガンド構造の重ね合わせから、共通する結合を基準に互いのフラグメント構造を入れ替えることで、新しい構造を生成します。
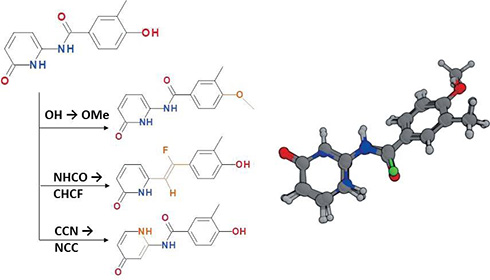
変換ルールに基づき既存リガンドを自動変換。右は変換後の3次元構造。
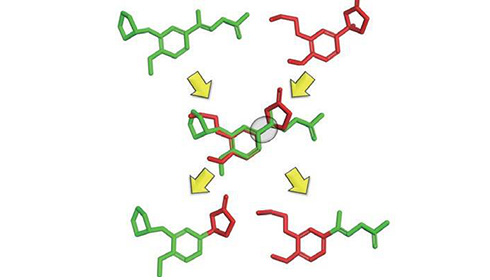
BREEDによる新規リガント設計。入力化合物(上段)を重ね合わせ(中段)、結合が重なる部分で置換基を交換(下段)。
- ※1
- ※2Lauri, G. ; Bartlett, P. A. CAVEAT: A Program to Facilitate the Design of Organic Molecules. J. Comput. Aided Mol. Des. 1994, 8, 51-66.
- ※3Pierce, A. C. ; Rao, G. ; Bemis, G. W. BREED: Generating Novel Inhibitors through Hybridization of Known Ligands. Application to CDK2, P38 and HIV Protease. J. Med. Chem. 2004, 47, 2768-2775.
統合計算化学システムMOE に関するお問い合わせ
-
Webでのお問い合わせ
入力フォーム当社はセキュリティ保護の観点からSSL技術を使用しております。
-
お電話でのお問い合わせ
富士通コンタクトライン(総合窓口)
0120-933-200(通話無料)受付時間:9時~12時および13時~17時30分(土曜・日曜・祝日・当社指定の休業日を除く)
